
所(园)在落羽杉属叶绿体比较基因组学研究方面取得阶段性进展
掌握落羽杉属的叶绿体基因组将有助于落羽杉属种质资源的开发利用,但是目前关于落羽杉属的叶绿体基因组特征的研究还是一片空白。我们测定了落羽杉、池杉、墨西哥落羽杉的完整叶绿体基因组全长,长度范围为131947bp~132613bp,三个叶绿体基因组均能编码120个基因,且120个基因在三个物种中排序一致。不同于典型的叶绿体基因组四分结构,落羽杉属叶绿体基因组丢失了反向重复区(IR)。最长的小IR为282bp,包含trnQ,参与异构体的形成。比较3个物种叶绿体基因组,发现91.57%的插入缺失indels会导致串联重复序列(TR)重复次数发生改变,而72.46%的单核苷酸多态性(SNPs)分布于TRs附近,说明TR可能与落羽杉属的叶绿体基因组突变动力学有关。本研究还挑选出11个高变区作为DNA条形码发展的候选区域,其中一个高变区Ycf1是唯一一个具有indel的编码区域,该indel由一个长TR组成。纵观整个广义柏类,Ycf1基因普遍包含TR的插入事件,且ycf1基因的长度得到广泛地扩张。同时ycf1也处于广义柏类叶绿体基因组的重排热点。所有以上特征都预示重复序列可能在叶绿体基因组进化中发挥着重要作用。本研究为重复序列在叶绿体基因突变和重排的动力学机制中的作用提供有力支持。此外,获得重复序列TRs和高变区的信息将有助于今后对落羽杉属和其他广义柏类植物的鉴定、系统发育分析和了解其种群结构和生物多样性提供分子依据。撰写的论文“Comparative chloroplast genomics of the genus Taxodium”发表于期刊BMC Genomics。
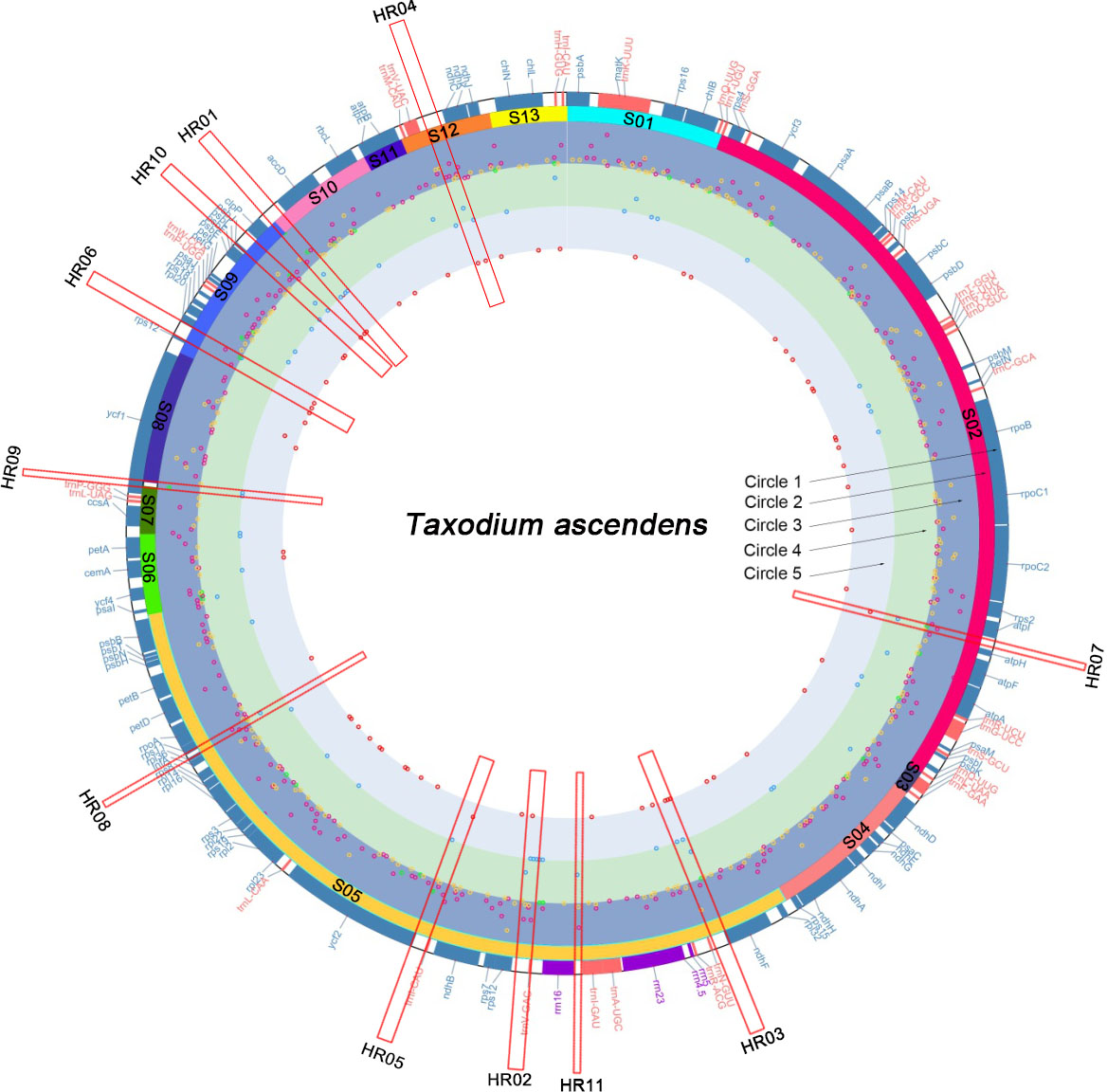
图1池杉叶绿体种保守基因块,TRs,indels的分布图
圈1:蓝色为池杉中编码基因,红色tRNA,紫色rRNA。圈2:池杉相对于苏铁叶绿体基因组的保守基因块。圈3:phobos软件报告的639个TR的位置。不同长度的TRs用不同的颜色标记,绿色代表重复≥20bp,瑰红色代表10〜19 bp,橙色代表<10 bp,图中点位置的相对高度表示200 bp的非重叠区域内多态位点的相对数量,分别统计处理三种不同颜色的重复,相对位置较高的点表示200 bp窗口内属于TR的更多基因块。圈4:indels分布(蓝色)。圈5:SNP分布(红色),相对位置较高的点表示在200 bp范围内有更多的多态位点。红色矩形(HR01-HR11)显示了11个挑选出的高变区的位置,矩形框内 Indel或SNP内部矩形的点的数量或相对位置高于外部。
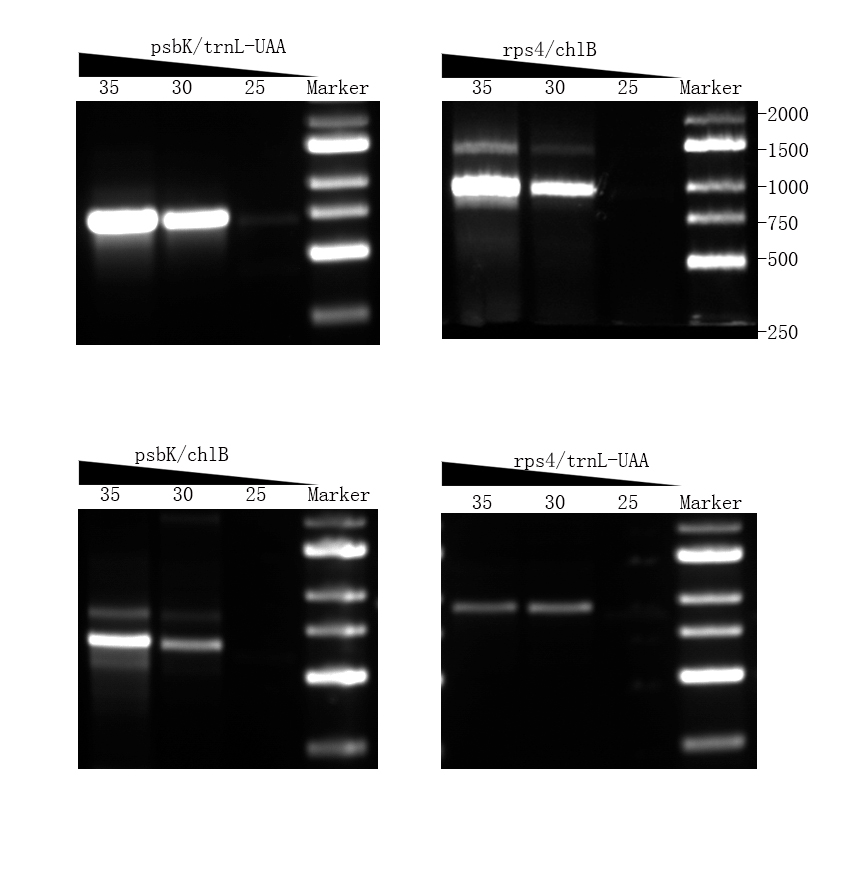
图2 池杉中两种异构体的电泳图

图3 针叶树中ycf1基因的串联重复序列分布图
注: 使用Mafft基于ycf1基因的序列比对构建系统发育树。 系统发育树的右侧显示了ycf1基因上串联重复序列的位置,根据多重序列比对的长度绘制水平线的长度,其中包括的基因裂隙长度。 因此,不同物种中重复序列的位置可以相互映射。 图最右边是ycf1基因的实际长度(不包括基因裂隙)
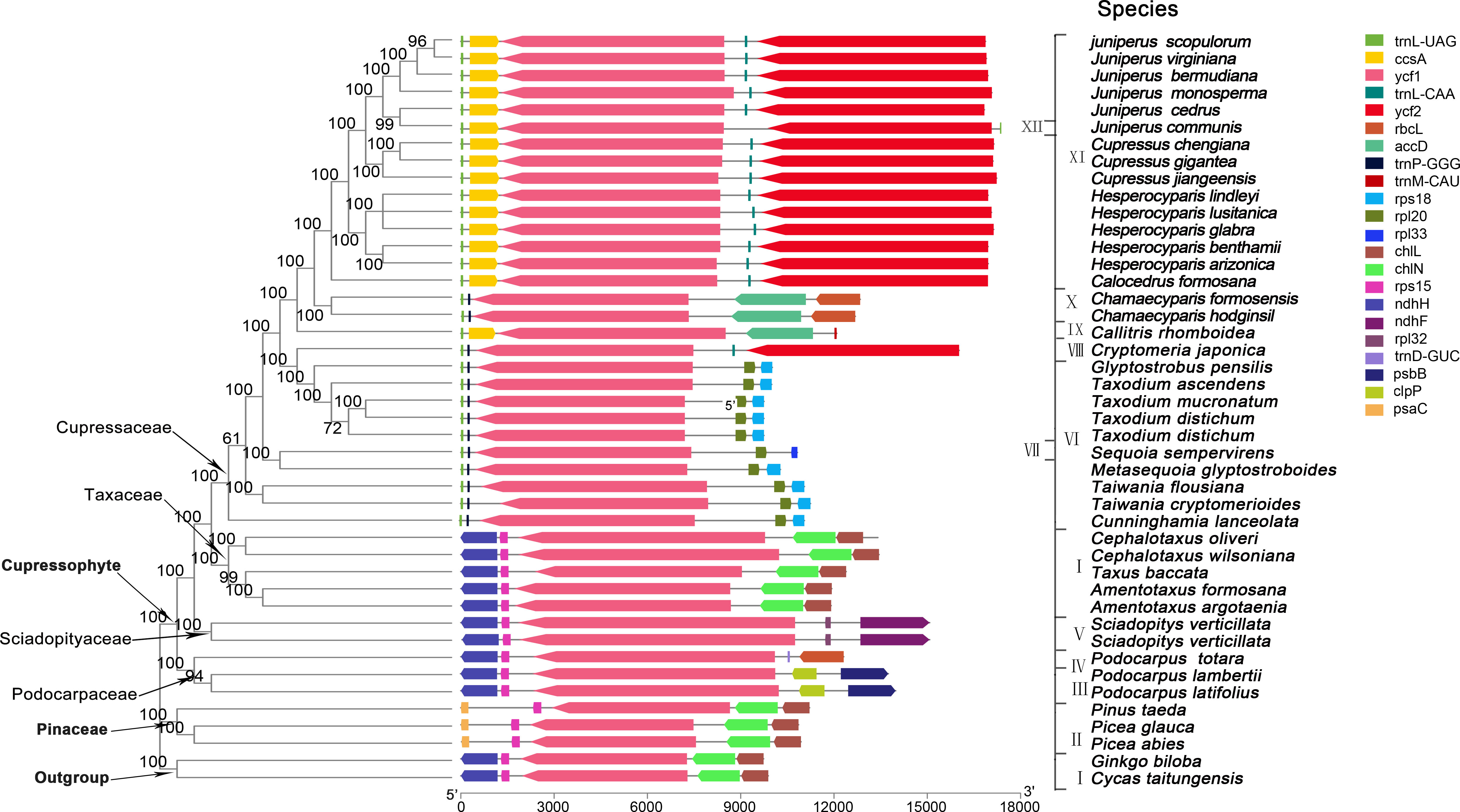
图4.ycf1基因周围的基因分布图
